Giới thiệu tài liệu
Tài liệu này cung cấp một cái nhìn tổng quan về các phương pháp giải trình tự DNA, từ những kỹ thuật cơ bản đến các công nghệ tiên tiến hiện nay.
Đối tượng sử dụng
Tài liệu này hướng đến sinh viên, nghiên cứu viên và các chuyên gia trong lĩnh vực sinh học phân tử, di truyền học, công nghệ sinh học và tin sinh học, những người quan tâm đến các phương pháp và ứng dụng của giải trình tự DNA.
Nội dung tóm tắt
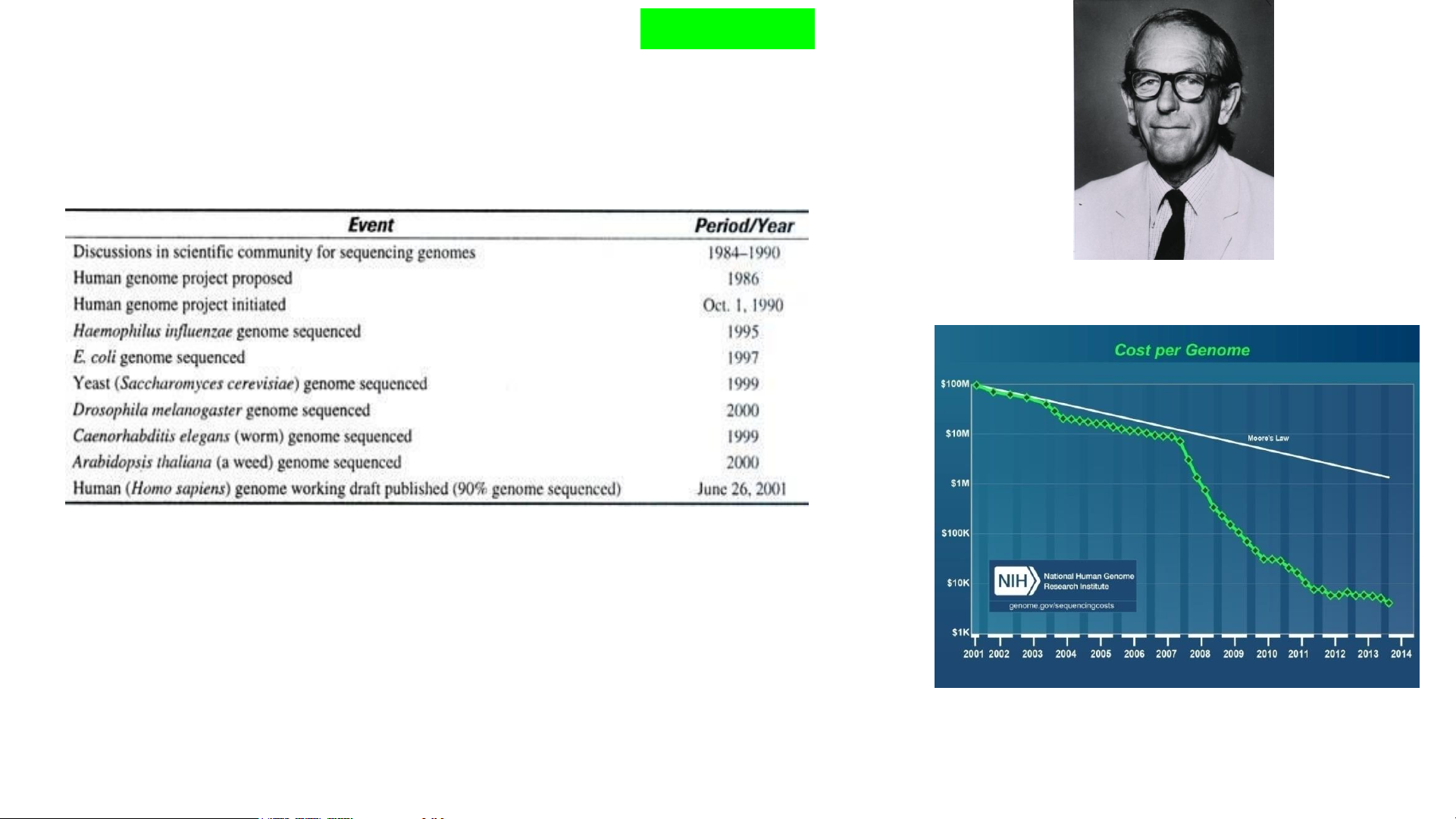
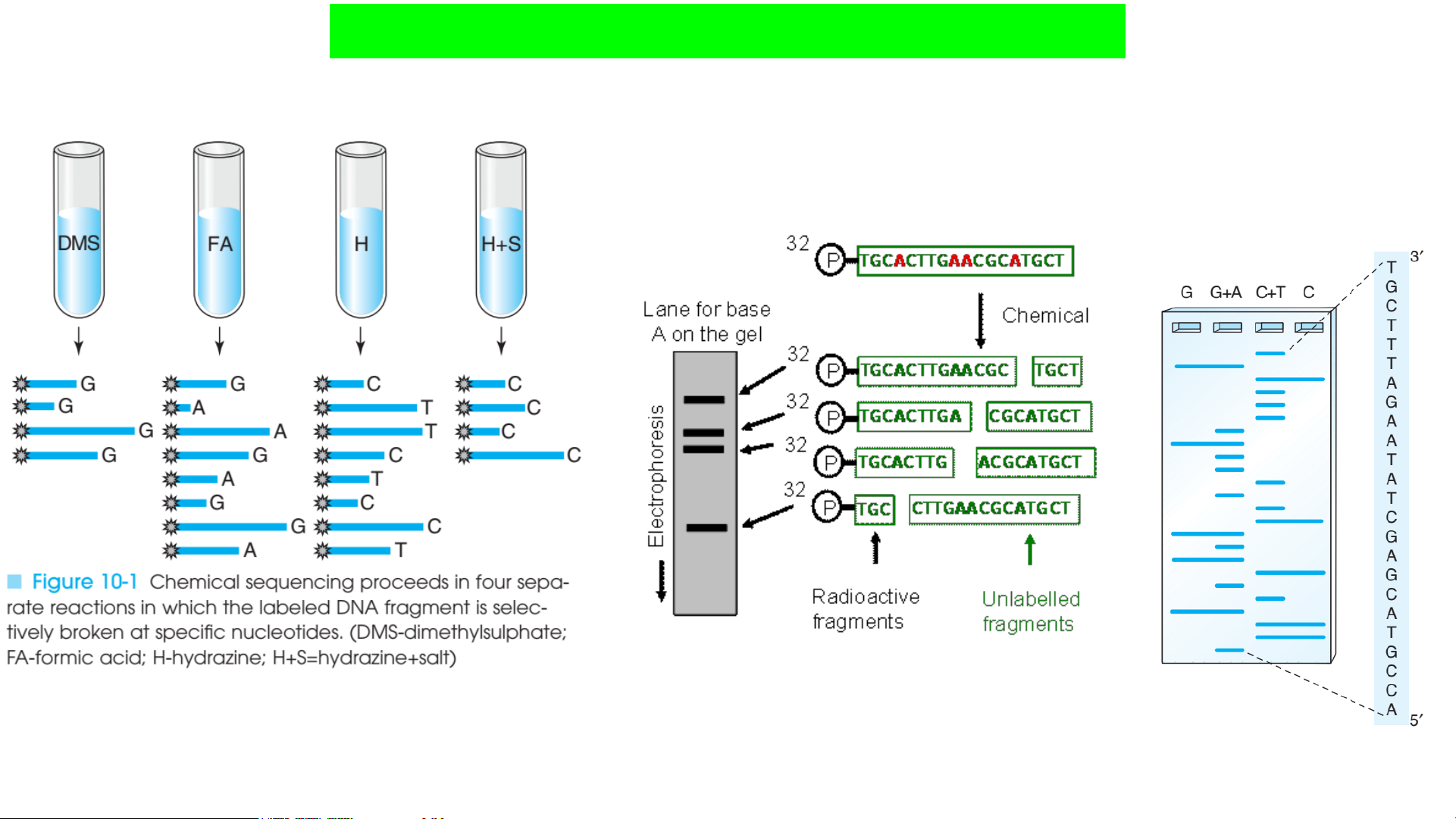
Tài liệu này trình bày chi tiết về lịch sử và sự phát triển của các phương pháp giải trình tự DNA. Bắt đầu với các kỹ thuật giải trình tự truyền thống như phương pháp Maxam-Gilbert, dựa trên sự phân cắt hóa học đặc hiệu tại các base, và phương pháp Sanger, sử dụng nguyên lý tổng hợp mạch bị dừng bởi các dideoxynucleotide (ddNTPs). Tài liệu phân tích ưu nhược điểm của từng phương pháp, bao gồm kích thước đoạn đọc, khả năng tự động hóa và hóa chất sử dụng. Tiếp theo, tài liệu giới thiệu về sự ra đời và phát triển mạnh mẽ của giải trình tự thế hệ mới (NGS), còn được gọi là giải trình tự song song khối lượng lớn. NGS đã cách mạng hóa lĩnh vực sinh học phân tử bằng cách cho phép giải trình tự hàng triệu đến hàng tỷ đoạn DNA cùng lúc, giảm đáng kể chi phí và thời gian. Các công nghệ NGS được đề cập bao gồm Pyrosequencing (ví dụ: Roche 454), Sequencing by Ligation (SOLID), Ion Torrent (dựa trên sự thay đổi pH), Illumina (dựa trên tổng hợp), PacBio SMRT (giải trình tự thời gian thực phân tử đơn) và Oxford Nanopore (dựa trên sự thay đổi dòng điện qua lỗ nano). Mỗi nền tảng được mô tả về nguyên lý hoạt động, đặc điểm kỹ thuật như chiều dài đoạn đọc, tỷ lệ lỗi và ứng dụng. Cuối cùng, tài liệu trình bày các ứng dụng đa dạng của giải trình tự DNA trong nghiên cứu và chẩn đoán, bao gồm giải trình tự toàn bộ hệ gen, exome, hệ phiên mã (transcriptome), hệ vi sinh vật (metagenome), và các phân tích chuyên sâu khác, minh họa vai trò thiết yếu của các kỹ thuật này trong sinh học và y học hiện đại.









![Bài giảng Sinh học di truyền ThS. Võ Thị Yến Nhi [chuẩn nhất]](https://cdn.tailieu.vn/images/document/thumbnail/2024/20240910/gaupanda051/135x160/1339607967.jpg)



















